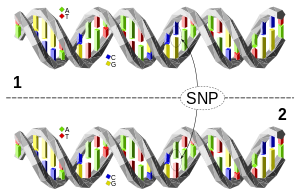
Un polymorphisme de nucléotide unique (SNP, prononcé snip ; plusieurs snips) est une variation de la séquence d'ADN dans une population. Un SNP n'est qu'une différence d'un seul nucléotide dans le génome.
Par exemple, les fragments d'ADN séquencés de deux personnes, AAGCCTA à AAGCTTA, sont différents dans un seul nucléotide. Dans ce cas, on dit qu'il y a deux allèles. Presque tous les SNP communs n'ont que deux allèles. Les SNP se trouvent le plus souvent dans des régions de l'ADN qui n'affectent pas la survie de l'organisme : sinon, ils seraient éliminés par la sélection naturelle. D'autres facteurs, comme la recombinaison génétique et le taux de mutation, peuvent également affecter la densité des SNP. Il existe des variations entre les populations humaines, de sorte qu'un allèle de SNP qui est commun dans un groupe géographique ou ethnique peut être beaucoup plus rare dans un autre.
Ces variations génétiques entre les individus (en particulier dans les parties non codantes du génome) sont parfois exploitées dans le cadre de l'empreinte génétique, qui est utilisée en médecine légale. En outre, ces variations génétiques entraînent des différences dans notre sensibilité aux maladies. La gravité de la maladie et la façon dont notre corps réagit aux traitements sont également des manifestations de variations génétiques. Par exemple, une mutation d'une seule base dans le gène de l'APOE (apolipoprotéine E) est associée à un risque plus élevé de maladie d'Alzheimer.